在生命科学探索的微观世界里,飞速发展的空间转录组技术宛如一台超广角百亿像素的“生命照相机”。它能够在单细胞甚至亚细胞分辨率下,捕捉组织中成千上万个基因的表达信息及其空间位置,为我们定格下生命在某一瞬间的精细画面。然而,生命的发育与演化本质上是一个连续流动的过程,就像一部跌宕起伏的电影。由于测序技术的破坏性本质,这台“照相机”只能拍摄一系列静态的“照片”(快照),而无法直接录制连续的视频。如何在这一系列离散、非配对甚至坐标系不一致的“照片”之间,通过算法重构出生命演化动态的“电影”,复原细胞分化、迁移和增殖的完整时空轨迹,是当前计算生物学领域亟待突破的难题 。
近日,北京大学前沿交叉学科研究院周沛劼研究员团队与北京大学数学学院李铁军教授团队在Nature Methods期刊上发表了题为 stVCR: Spatiotemporal dynamics of single cells的研究论文。该研究开发了一个名为stVCR (spatio-temporal Video Cassette Recorder) 的生成式深度学习模型。stVCR 创新性地结合了动态最优传输(Dynamical Optimal Transport, DOT)、刚体变换不变性以及不平衡最优传输理论,成功解决了不同时间点样本的空间坐标对齐难、细胞群体数量不平衡等关键挑战。该算法实现了从多张非配对的空间转录组快照中,端到端地同时重构细胞的连续分化、物理空间迁移以及增殖/凋亡过程,如同为静态的组织切片按下“播放键”,为解析复杂生物系统的时空演化机制提供了全新的计算范式 。

深度学习驱动的动态最优传输模型构建
在模型构建阶段,研究团队针对时空转录组数据的特性设计了三个核心模块。首先,针对基因表达数据,利用Wasserstein最优传输模拟分布的时间耦合;其次,针对细胞在物理空间中的位置变化,考虑到不同时间点样本可能存在的旋转和位移,采用了刚体变换不变的最优传输进行空间对齐;最后,针对发育过程中细胞分裂和凋亡导致的细胞数量变化,引入了不平衡最优传输来模拟种群动态。此外,stVCR 还允许整合已知的生物学先验知识(如细胞类型转换关系)和空间结构保持先验,以生成更具生物学意义的结果(图1)。stVCR 将细胞状态建模为随时间演化的分布。模型通过神经网络参数化求解包含细胞空间速度(物理迁移)、RNA速度(基因表达变化)和生长率(增殖/凋亡)的“运输-生长”偏微分方程。这种端到端的训练方式,使 stVCR 能够捕捉细胞在组织器官中演化的内在时空动力学规律,实现了对复杂生命过程的高保真还原 。

图1 stVCR算法框架概览
基于模拟数据的基准测试与鲁棒性验证
为验证 stVCR 在空间对齐与时空动态重构方面的稳健性,研究团队构建了包含特定基因调控回路的模拟数据集,并引入随机旋转扰动以模拟真实测序中组织切片的坐标差异。实验结果表明,stVCR 能够精准地将不同时间点的空间坐标统一映射至参考系,并高度还原细胞的基因表达演化、空间迁移路径及增殖速率。通过与主流基线方法对比,stVCR 在插值精度、速度场推断及生长率估计等方面均表现优异,证明了在动力学建模中耦合空间对齐与细胞生灭过程的必要性。
解析蝾螈脑再生的复杂时空机制
研究团队将 stVCR 应用于蝾螈脑再生的单细胞时空转录组数据,涵盖了损伤后 2, 5, 10, 15, 20 天等关键时间点。stVCR 成功重构了损伤响应和再生过程中的连续细胞轨迹(视频1)。
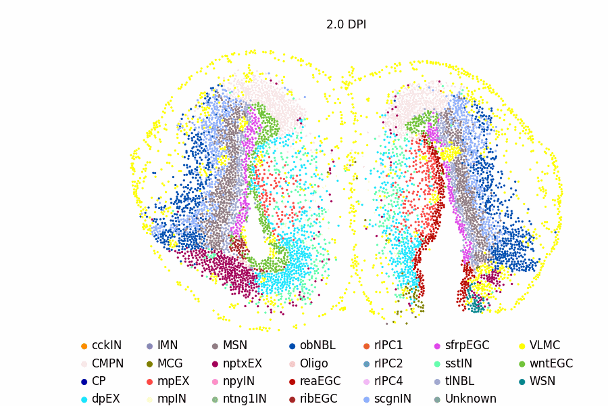
视频1 stVCR重构蝾螈脑再生时空动态过程
此外,stVCR还揭示了伤口处附近细胞的定向迁移,显著升高的细胞增殖速率以及构建了EGC类型细胞的连续发育谱系(图2)。
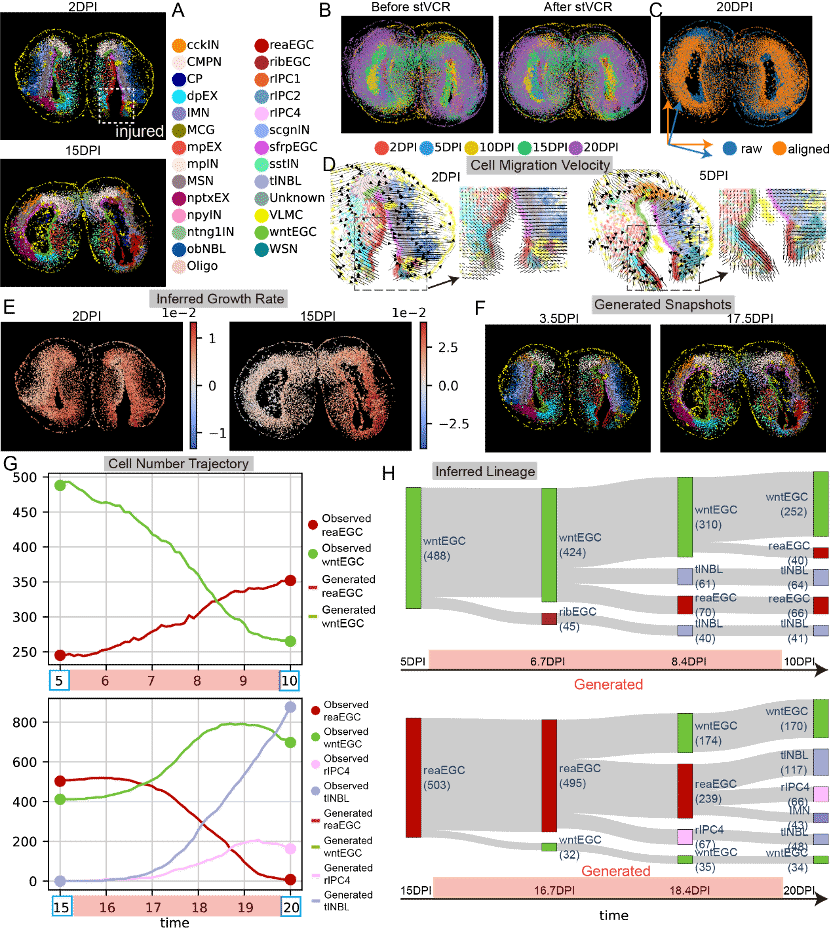
图2 stVCR重构蝾螈脑再生时空动态
挖掘基因-空间互作与调控网络
除了重构表型轨迹,stVCR 还能深入解析潜在的分子机制。通过计算物理迁移速度和生长率对基因表达的偏导数,研究团队识别出了 “迁移驱动基因”和“生长驱动基因”。GO富集分析表明这些基因与神经元迁移、细胞粘附调节及核糖体生物合成密切相关。此外,stVCR 推断的动态基因调控网络显示,关键基因之间的调控关系随时间发生动态变化,且受到细胞空间位置的显著影响,展示了其在解析复杂时空基因表达模式方面的解释能力(图3)。

图3 stVCR解析蝾螈脑再生的基因层面机制
结合生物学先验重构3D果蝇胚胎发育
针对真实实验中采样时间点稀疏的痛点,stVCR 提供了整合生物学先验知识的灵活接口。在仅包含两个时间点的 3D 果蝇胚胎发育数据分析中,该方法通过引入组织结构保持先验与发育流向约束,精准构建了符合生物规律的连续三维轨迹。结果不仅清晰刻画了中枢神经系统细胞在胚胎内部的迁移路径与形态发生过程,且相较于传统静态最优传输方法,stVCR 生成的中间状态展现出更优的时空连贯性,有效避免了非物理性的细胞跳跃或轨迹断裂(视频可见文章补充材料)。
综上所述,研究提出的 stVCR 算法通过创新的动态最优传输框架,为时空转录组数据提供了一套统一的生成式建模方法。它不仅克服了“快照”数据的局限性,成功录制了细胞生命活动的“动态电影”,还深入揭示了基因表达与空间位置之间复杂的相互作用机制。stVCR 的建立为发育生物学、再生医学及疾病演化研究提供了强有力的计算工具,具有广阔的应用前景。stVCR也是李铁军/周沛劼计算生物学团队近年来继MuTrans(Nature Communications 2021)、STT(Nature Methods 2024)和RNA Velocity的数学理论(CSIAM-AM 2021/2024)等工作之后,对单细胞时空转录组数据采用动力学方法进行分析的又一重要进展。在方法论层面,团队还系统发展了面向组学数据动态建模与生成任务的AI计算框架,代表性工作包括DeepRUOT (ICLR 2025 Oral), VarRUOT (NeurIPS 2025), CytoBridge (NeurIPS 2025),WFR-FM(ICLR 2026)等,为构建具有动态演化解析能力的AI虚拟细胞提供了思路。
北京大学数学科学学院博士生彭强威为该研究论文的第一作者。北京大学前沿交叉学科研究院周沛劼研究员与北京大学数学科学学院李铁军教授为该论文的共同通讯作者。该研究工作得到了国家自然科学基金委“科学计算与机器学习”科学中心项目(基金号12288101),科技部国家重点研发计划(基金号2021YFA1003301)和国家自然科学基金委优秀青年科学基金(海外)资助。相关计算在北京大学高性能计算校级公共平台进行。
论文链接:https://www.nature.com/articles/s41592-026-03010-3